Biochemische Reaktionen
E N D
Presentation Transcript
1. Biochemische Reaktionen
2. Gliederung
Einf�hrung
Das Massenwirkungsgesetz
Enzyme
3.1 Enzymkinetik
3.2 Modelle
3.2.1 Gleichgewichtsapproximation
3.2.2 Quasi � Stationarit�tsapproximation
3.3 Enzyminhibition
3.3.1 kompetitive Inhibition
3.3.2 allosterische Inhibition
3.3.3 Kooperativit�t
3.4 Das Monod � Wyman � Modell
4. Glykolyse und Glykolytische Oszillation
3. 1. Einf�hrung
4. Reaktionsgeschwindigkeit
Die Geschwindigkeit, mit der eine reagierende Substanz verbraucht oder mit der ein Reaktionsprodukt gebildet wird
Sie ist abh�ngig von:
Zahl der Zusammenst��e pro Zeiteinheit
Anteil mit ausreichender Kollisionsenergie
Anteil mit geeigneter Orientierung
Geschwindigkeitskonstante
durch das Symbol k darstellbar
Stellt die Proportionalit�t der Reaktionsgeschwindigkeit v zu den Konzentrationen der Substrate dar
v = k1[A] Reaktion 1. Ordnung
v = k2[A][B] Reaktion 2. Ordnung
abh�ngig von der geometrischen Struktur und Gr��e der reagierenden Molek�le & der Temperatur
Reaktionsrate
Sie gibt an, wie oft die chemischen Reaktionen pro Zeiteinheit im
Einheitsvolumen stattfinden:
Sie ist somit proportional zur Anzahl der Zusammenst��e pro Zeiteinheit zwischen Edukten
1. Einf�hrung
5.
Reaktion 1. Ordnung
A ? B
die Reaktionsgeschwindigkeit ist proportional zur Konzentration von A
Reaktion 2. Ordnung
A + B ? C + D
die Reaktionsgeschwindigkeit h�ngt von der Konzentration zweier Reaktionsteilnehmer abh�ngt
1. Einf�hrung
6. 2. Das Massenwirkungsgesetz
A + B ??? C
Reaktionsrate:
? Massenwirkungsgesetz (MWG)
Die Reaktionskonstante verdoppelt sich nicht zwingend mit der Verdoppelung der Konzentration eines Substrats
7. A + B C
die Konzentrations�nderung von A f�r die Reaktion lautet:
= k-[C] � k+[A][B]
im Gleichgewichtszustand �ndern sich die Konzentrationen nicht, es gilt:
[C]eq = [A]eq[B]eq
sind A und C an keinen weiteren Reaktionen beteiligt,
so gilt [A] + [C] = A0 (const.)
? [C] = A0
Keq = k-/k+ hei�t Gleichgewichtskonstante
2. Das Massenwirkungsgesetz
8. 2. Das Massenwirkungsgesetz
Keq hat keine feste Einheit, sie richtet sich nach der jeweiligen Reaktionsgleichung
Keq <<1 ? hohe Affinit�t zwischen A und B
[B] = Keq: die H�lfte von A liegt in gebundener Form vor
9. 2. Das Massenwirkungsgesetz
Das MWG gilt f�r reversible Reaktionen, die den
Gleichgewichtszustand erreicht haben.
Es gibt den Zusammenhang zwischen den
Aktivit�ten der Edukte und der Produkte einer
Reaktion im chemischen Gleichgewicht an.
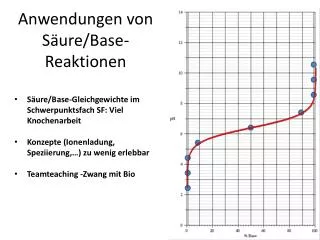
10. 3. Enzyme
�http://www.webmed.ch/Archiv_akuelle_Meldungen/Archiv_Bilder/catalase2%20(Enzym).gif�
11. 3.1. Enzymkinetik
Enzyme sind
die am h�chsten spezialisierten Proteine
hochspezifisch
Katalysatoren biologischer Reaktionen
f�r sie gilt:
sie arbeiten unter milden Bedingungen in w�ssrigen L�sungen
sie helfen anderen Molek�len, sich in ein Produkt umzuwandeln, sie selbst ver�ndern sich nicht
Wichtigste Eigenschaften: Genauigkeit und katalytische Wirkung
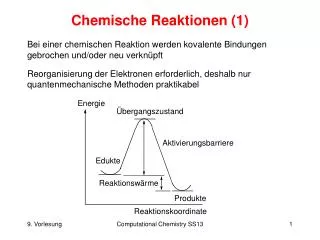
12. Sie setzen die Aktivierungsenergie herab und beschleunigen so die Bildung des Produkts
bis zu 10Mio mal schnellere Reaktionen
Enzyme folgen nicht direkt dem MWG, die Reaktionsrate steigert sich mit der Enzymkonzentration nur in einem gewissen Umfang, bis die maximale Reaktionsgeschwindigkeit erreicht ist
3.1 Enzymkinetik
13. 3.2. Modelle S + E C P + E
Enzyme beschleunigen die Hin- und R�ckreaktion
Es gibt zwei �hnliche Arten, die Gleichung zu bestimmen
Die Gleichgewichtsapproximation
(Michaelis und Menten)
Quasi � Steady � State Approximation
(Briggs und Haldane)
14. s = [S], c = [C], e = [E] und p = [P]
= k-1c - k1se
= (k-1 + k2)c � k1se
= k1se � (k2 + k-1)c
= k2c
e + c = e0 3.2. Modelle
15. 3.2.1 Die Gleichgewichtsapproximation
S + E C P + E
Annahme: das Substrat seht unmittelbar im Gleichgewicht mit dem Komplex ? k1se =k-1c
mit e + c = e0 ergibt sich: (Ks = k-1/k1)
die Reaktionsrate ist gegeben durch
Vmax= k2e0 ist die max. Reaktionsgeschwindigkeit
wird erreicht, wenn sich alle Enzyme mit dem Substrat S im Komplex befinden
16. 3.2.1 Die Gleichgewichtsapproximation
bei s = Ks hat die Reaktionsrate die H�lfte ihres Maximums erreicht
Wichtig: die Gleichung k1se = k-1c ist nicht immer g�ltig, denn nach der Gleichung = k-1c - k1se w�rde das Substrat nicht verbraucht werden und kein Produkt entstehen
17. 3.2.2 Quasi � Stationarit�tsapproximation Annahme: die Bildung und der Zerfalls des Komplexes stehen zu jeder Zeit im Gleichgewicht
? dc/dt � 0
Einf�hrung dimensionsloser Variablen
s = x = t = k1e0t
? = ? = a =
= -s + x (s +a)
= s � x (s +?)
18. = -s + x(s +a) = s - x(s +?)
= 0 ? = 0
II
Quasi - Stationarit�tsapproximation:
die rechte Seite der Gleichung wird Null gesetzt
? Variable x �ndert sich mit s
sie ber�cksichtigt: ? ist klein und dx/dt hat die Ordnung 1 3.2.2 Die Quasi - Stationarit�tsapproximation
19. Aus =0 folgen die DGL�s
und � Michaelis � Menten � Gesetz�
q = ?-a =
Mit Hilfe der urspr�nglichen Variablen:
Km = 3.2.2 Die Quasi - Stationarit�tsapproximation
20. 3.2.2 Die Quasi - Stationarit�tsapproximation Quasi � Stationarit�tszustand Gleichgewicht
Km =
? �hnliche Form, Ergebnisse basieren jedoch auf unterschiedliche Annahmen
21. 3.2. Modelle Michaelis � Menten � Gesetz ist eine brauchbare Approximation, wie das MWG nicht universell anwendbar
Km ist relativ einfach zu bestimmen, denn
kann geschrieben werden als
? 1/V ist eine lineare Funktion von 1/s.
22. 3.2. Modelle
Diese doppeltreziproke Auftragung wird Lineweaver � Burk � Plot genannt
Sie werden experimentell bestimmt
Man kann an ihnen Vmax und Km ablesen
23. 3.2. Modelle Alternative Methode: der direkte lineare Graph, Vmax gegen Km
Wiederholen des Versuchs mit diversen Anfangskonzentrationen und Geschwindigkeiten ergibt eine Familie von Geraden
Idealfall: Schnittpunkt in einem einzelnen Punkt
http://de.wikipedia.org/w/index.php?title=Datei:Enzymkinetik3.png&filetimestamp=20090302154106
24. 3.3. Enzyminhibition
Hemmt die katalytische Wirkung
Allgemeine Eigenschaft von Enzymreaktion
wichtig zur Kontrolle der Enzymaktivit�t
irreversible Hemmstoffe oder katalytische Gifte: sie senken die Enzymaktivit�t auf 0
Das Enzymmolek�l ist f�r gew�hnlich ein sehr langes Protein, meist weitaus l�nger als das Substratmolek�l, dessen Reaktion katalysiert wird
25. 3.3. Enzyminhibition Im Enzym eingebunden sind ein oder mehr aktive Zentren, an die sich das Substrat binden kann, um einen Komplex zu bilden
Allgemein katalysiert ein Enzym ein Substratmolek�l �hnlicher Struktur (Schl�ssel-Schloss-Prinzip)
http://www.scheffel-gymnasium.de/faecher/science/biologie/proteine_enzyme/2enzym/enzym.htm
Gibt es ein dem Substrat �hnliches Molek�l, kann dieses ebenfalls an die aktive Seite gebunden werden und so die Bindung des Substratmolek�ls verhindern und die Reaktion hemmen
26.
kompetitiver Hemmstoff: der Hemmstoff wetteifert mit dem Substrat um die aktive Seite
3.3. Enzyminhibition
27. Das Enzym hat h�ufig andere bindende Seiten, die sich von der aktiven Seite unterscheiden - allosterische Seite? sie unterscheiden sich strukturell von der katalytisch aktiven Seite
�regulierende Seiten�, da die katalytische Aktivit�t durch Bindung an diese Seite reguliert wird
Effektor (Modifier):der Liganden, der an die allosterische Seite gebunden ist
Der Effektor hei�t allosterischer Aktivator, wenn er die katalytische Wirkung steigert und allosterischer Inhibitor, wenn er die Aktivit�t des Substrats mindert 3.3. Enzyminhibition
28. 3.3.1 Kompetitive Inhibition Einfachstes Beispiel: die Reaktion wird gestoppt, wenn der Inhibitor an die aktive Seite des Enzyms gebunden ist
S + E C1 E + P
E + I C2
Mit Hilfe des MWG
= -k1se + k-1c1
= -k3ie + k-3c2
= k1se � (k-1 + k2)c
= k3ie � k-3c2
e + c1 + c2 = e0
29. Im Quasi-station�ren Zustand
f�r die Reaktionsgeschwindigkeit ergibt sich
Der Effekt des Inhibitors ist es, die effektive Gleichgewichtskonstante des Enzyms durch den Faktor 1+i/Ki zu steigern
? die Reaktionsgeschwindigkeit nimmt ab
30. Falls der Inhibitor sich an die allosterische Seite binden kann, ergibt sich die M�glichkeit, dass das Enzym den Inhibitor und das Substrat gemeinsam binden
vier m�gliche Bindungsarten f�r das Enzym und �berg�nge zwischen ihnen
E ES E + P
EI EIS 3.3.2 Allosterische Inhibition
31. 3.3. Enzyminhibition Die einfachste Analyse ist die Gleichgewichtsanalyse
definiere und
x, y, z beschreiben die Konzentrationen von ES, EI und EIS
Aus dem MWG folgt f�r den station�ren Zustand
? lineares Gleichungssystem
32. 3.3. Enzyminhibition Wir k�nnen x, y, z als Funktionen von i und s bestimmen
mit Vmax = k2e0 ist
der allosterische Inhibitor mindert die maximale Reaktionsgeschwindigkeit, w�hrend Ks unver�ndert bleibt
33. 3.3.3 Kooperativit�t Ein Enzym kann mehr als ein Substratmolek�l binden
Bindung eines Substratmolek�ls beeinflusst die Bindung des nachfolgenden
Annahme:ein Enzym kann zwei Substratmolek�le binden ? es kann in einem von drei Stati existieren
Als freies Molek�l E
Als Komplex mit einem besetzten Center C1
Als Komplex mit zwei besetzten Center C2
S + E C1 E + P
S + C1 C2 C1 + P
34. 3.3.3 Kooperativit�t Das MWG angewandt, kann man die Gleichungen f�r die 5 Konzentrationen von S, E, C1, C2 und P aufschreiben
35. Wir �bernehmen die Annahme des Quasi-station�ren Zustands: dc1/dt = dc2/dt = 0
F�r die Reaktionsgeschwindigkeit ergibt sich
3.3.3 Kooperation
36. 3.3.3 Kooperation Die aktiven Seiten handeln unabh�ngig und identisch voneinander
? k1 = 2k3 = 2k+, 2k-1 = k-3 = 2k- und 2k2 = k4
F�r die Reaktionsgeschwindigkeit ergibt sich
37. Die Bindung des ersten Substratmolek�ls erfolgt langsam, die zweite sehr schnell (gro�e positive Kooperativit�t)
k3 ? 8 und k1 ? 0, k1k3 = const.
? K1 ? 8 und K2 ? 0, K1K2 =const.
Km� = K1K2 und Vmax = k4e0
i.A. gibt es n Gleichgewichtskonstaten, wenn n Substratmolek�le an das Enzym gebunden sind
? K1 ? 8 und Kn ? 0, K1Kn = const.
wobei Kmn =
Diese Gleichung ist bekannt als Hill � Gleichung 3.3.3 Kooperation
38. es gilt
? das Hill � Diagramm sollte eine Gerade mit der Steigung n ergeben
es ist nicht ungew�hnlich, dass n nicht ganzzahlig ist
3.3.3 Kooperation
39. 3.3.3 Kooperation ein Enzym kann negative Kooperativit�t aufweisen
? k3 wird herabgesetzt
40. 3.4. Das Monod � Wyman � Changeux Modell das Modell basiert auf folgende Annahmen:
? kooperative Proteine sind zusammengesetzt aus diversen identischen Reaktionseinheiten, genannt Protomer, die die gleichen Positionen im Protein belegen
? jedes Protomer umfasst eine bindende Seite f�r jeden Liganden
? die bindenden Seiten innerhalb jeden Proteins sind �quivalent
? falls die Bindung eines Linganden zu einem Protomer einen konformativen Wechsel im dem Protomer einleitet, wird ein identischer konformativer Wechsel in allen Proteinen eingeleitet
? das Protein hat zwei konformative Stati, gew�hnlich bezeichnet als R und T, die sich in ihrem Verhalten Liganden zu binden unterscheiden
41. wir betrachten Protein, mit nur zwei binden Seiten
es kann in einem von 6 Stati existieren:
Ri, i= 0, 1, 2 oder
Ti, i= 0, 1, 2
der Einfachheit halber: Ri kann nicht in Ti umgerechnet werden
Die Stati f�r das Protein und die zugelassenen �berg�nge
3.4. Das Monod � Wyman � Changeux - Modell
42. es gilt ri und ti sind die entsprechenden Konzentrationen von Ri und Ti
f�r die S�ttigungsfunktion gilt:
mit Ki = k-i/ki, i=1, 2, 3 ergibt sich
durch Substitution erh�lt man
wobei r0/t0 = K2
3.4. Das Monod � Wyman � Changeux - Modell
43. 3.4. Das Monod � Wyman � Changeux - Modell Allgemein ist Y eine sigmoidale Funktion von s
K3 = 8 ? das Substrat kann nicht direkt an die T- Konformation
binden
?
K2 = 8 ? nur die R � Konformation existiert
? Michaelis � Menten Gleichung
44. 4. Glykolyse und glykolytische Oszillation Stoffwechsel kann als Austausch freier Energie gesehen werden
Stoffwechselwege: die durch Enzyme katalysierten Auf-/Ab- und Umbauprozesse in den Zellen
bekannter Tr�ger von Energie in der Zelle: ATP
Adenosintiphosphat
45. 4. Glykolyse und glykolytische Oszillation Die Bindungen der drei Phosphate sind sehr energiereich
Werden die Phosphoanhydrid-Bindungen durch Enzyme hydrolytisch gespalten, entsteht das Adenosindiphosphat (ADP) bzw. das Adenosinmonophosphat (AMP) und Phosphat
es werden jeweils etwa 32,3 kJ/mol (Spaltung einer Bindung) oder 64,6 kJ/mol (Spaltung beider Bindungen) Energie frei.
Die freiwerdende Energie erm�glicht die Arbeitsleistungen in den Zellen.
47. 4. Glykolyse und glykolytische Oszillation PFK 1 wird von ATP allosterisch gehemmt
? allosterisches Enzym
ATP kann Substrat und allosterischer
Hemmstoff sein
der Inhibitoranteil von ATP wird durch AMP beseitigt
? Aktivit�t von PFK1 steigt, wenn
ATP/AMP sinkt
2ADP ATP + AMP
48. 4. Glykolyse und glykolytische Oszillation ein �berfluss an Fructose 6-Phosphat f�hrt zur Bildung von Fructose-2,6-bisphosphat
? Aktivit�t von PFK1 w�chst
? negative R�ckkopplung
PFK1- Aktivit�t wird von einem komplexen System von Reaktionen kontrolliert
49. 4. Glykolyse und glykolytische Oszillation unter gewissen Umst�nden ist bekannt:
die Rate der Glykolyse ist periodisch, manchmal sogar chaotisch
ein mathematisches Modell von Sel�kov (1968), sp�ter modifiziert von Goldbeter und Lefever (1972)
Achtung: nur die positive R�ckkopplung von ADP auf PFK1 wird beachtet
50. 4.1. Modell von Sel�kov PFK1 ist inaktiv im ungebundenen Status
aktiviert durch die Bindung mit ADP-Molek�len
im aktiven Status katalysiert das Enzym die Produktion von ADP aus ATP
das Modell:
PFK1 (E) ist aktiviert oder deaktiviert, je nach Bindungsstatus mit den ?-Molek�len von ADP (S2)
?S2 + E ES2?
ATP (S1) kann sich an die aktivierte Form des Enzyms binden um ein Produkt von ADP zu bilden
Annahme: die Rate von S1 ist best�ndig, das Produkt S2 wird jedoch irreversibel verbraucht
51. 4.1. Modell von Sel�kov ? S1
S1 + ES2? S1ES2? ? ES2? + S2
S2 ?
52. 4.1. Modell von Sel�kov s1 = [S1], s2 = [S2], e = [E], x1 = [ES2?], x2 = [S1ES2?]
e + x1 + x2 = e0
53. 4.1. Modell von Sel�kov
es ergibt sich
mit
54. 4.1. Modell von Sel�kov Annahme: ? ist klein ? u1 und u2 sind fest und k�nnen als ihre Quasi � Stationarit�tsgr��en gesetzt werden
55. 4.1. Modell von Sel�kov das System hat periodische L�sungen f�r einen gewissen Bereich von ?
wegen der S�ttigung, ist die Funktion f(s1, s2) durch 1 begrenzt
falls ? > 1, sind die L�sungen der Differentialgleichungen nicht begrenzt
56. 4.1. Modell von Sel�kov 0 < ? < 1
die Hauptisoklinen des Phasenflusses sind gegeben durch
57. 4.1. Modell von Sel�kov f�r die station�re L�sung gilt:
die Stabilit�t der konstanten L�sung findet man durch Linearisierung der DGL�s der station�ren L�sung und Pr�fung der Eigenwerte des linearen Gleichungs-systems
58. 4.1. Modell von Sel�kov das linearisierte System hat die Form:
die charakteristische Gleichung f�r die Eigenwerte ? der linearen Gleichungssysteme ist
Da f1 immer positiv ist, ist die Stabilit�t des linearen Systems durch das Vorzeichen von H= af2 � ? � f1 betimmt
es ist stabil f�r H < 0 und instabil, falls H > 0
59. Wechsel der Vorzeichen, gibt es bei H = 0
dies sind Hopf � Bifurkationen periodischer L�sungen mit einer approximativen Frequenz
? H(0) = ?(?-1) H(1) = -?
? f�r ? > 1 muss es einen Hopf-Bifurkationspunkt geben, unter dem die konstante L�sung instabil ist
4.1. Modell von Sel�kov
60. 4.1. Modell von Sel�kov f�r ? kurz unterhalb des Bifurkationspunktes, gibt es eine stabile periodische Bahn
61. 4.2. Hess und Boiteux Hess und Boiteux (1973):
es gibt f�r hohe und niedrige Injektionsraten eine stabile Stationarit�sl�sung
es gibt zwei Hopf � Bifurkationspunkte
1. bei 20mM/hr Dauer 8Min
2. bei 160mM/hr Dauer 3Min
62. 4.3. Goldbeter und Lefever sie schlugen 1972 Modell des Monod � Wyman � Changeux � Typs vor
Annahme: PFK1 ist ein Dimer, das in zwei Stati existiert
aktiven Status R
inaktiver Status T
S1 kann an beide Formen gebunden werden
S2 (positiver Effektor des Enzyms) bindet nur an die aktive Form
63. 4.3. Goldbeter und Lefever Die enzymatischen Formen, an die ein Substrat binden, zersetzen sich irreversibel, um ADP zu bilden
das Substrat wir dem System in einer konstanten Rate geliefert
die Rate der R�ckbildung des Produkts verl�uft proportional zur Konzentration
64. 4.3. Goldbeter und Lefever Tj = inaktive T-Form von der Enzymbindung zu j Substratmolek�len
Rij = aktive R-Form des Enzyms, gebunden an i Substratmolek�le und j Produktmolek�len
65. 4.3. Goldbeter und Lefever das Substrat S1 h�lt das System im inaktiven Status durch Bindung mit T0 um T1 zu bilden
S2 h�lt das System im aktiven Status
durch Bindung mit R00 um R01 zu bilden
durch Bindung mit R01 um R02 zu bilden
66. 4.3. Goldbeter und Lefever mit Hilfe des MWG erhalten wir die Differentialgleichungen der 14 Arten
67. 4.3. Goldbeter und Lefever
Annahme: die 12 Zwischenstufen sind im Quasistationarit�szustand
? lineares Gleichungssystem mit 12 Unbekannten und 12 Gleichungen
es ist l�sbar, wenn wir die Gesamtmenge der Enzyme e0 setzen
68. 4.3. Goldbeter und Lefever durch Substitution dieser L�sung in die Differentialgleichungen f�r s1 und s2 erhalten wir
wir f�hren dimensionslose Variablen ein
wir erhalten das System
69. 4.3. Goldbeter und Lefever Falls wir au�erdem annehmen
das Substrat bindet nicht an die T-Form (k3 = 0, T ist komplett inaktiv)
T0 wird R00 gegen�ber bevorzugt (k1>>k-1)
falls das Substrat S1 an die R-Form bindet, wird die Bildung des Produkts S2 der Trennung bevorzugt (k>>k-2)
? das System kann wesentlich vereinfacht werden
f(s1, s2) = s1(1 + s2)2
70. 4.3. Goldbeter und Lefever die Hauptisoklinen dieses Systems sind deutlich verschieden vom Sel�kov Modell
die eindeutige L�sung f�r die Stationarit�tsbedingung ist
71. 4.3. Goldbeter und Lefever Die Stabilit�t wird wieder von der charakteristischen Gleichung bestimmt und das Vorzeichen des Realteils der Eigenwerte ist das selbe wie von
ausgewertet unter Stationarit�tsbedingungen
sie kann auch geschrieben werden als Polynom dritten Gerades
72. 4.3. Goldbeter und Lefever f�r gen�gend gro�es ? hat das Polynom zwei Nullstellen, die gr��er sind als 2: y1 und y2
Annahame: die Flussrate ? ist proportional zur experimentellen Angebotsrate von Glucose
Forderung:
?
Am Hopf - Bifurkationspunkt, erhalten wir die Oszillationsperiode
theoretisch T1/T2 = 4,6
experimentell T1/T2 = 2,7
73. 4.3. Goldbeter und Lefever